Plusieurs de nos articles évoquent la technologie d’Oxford Nanopore, entre impatience et curiosité.
Plusieurs de nos articles évoquent la technologie d’Oxford Nanopore, entre impatience et curiosité.
Le principe de cette technologie : séquencer sans pré-amplification (il s’agit d’un séquenceur de 3ème génération) une molécule d’ADN en en hydrolysant les nucléotides élémentaires, qui passeront dans des pores. Ces pores seront couplés à des capteurs saisissant la signature singulière de chaque base constitutive de la molécule à séquencer. Jusqu’à présent le problème majeur sur lequel ont buté les ingénieurs d’Oxford Nanopore : accélérer la célérité d’acquisition des capteurs ou ralentir le passage des nucléotides au travers des pores -nucléotides qui, au départ, s’engouffraient à plus de 1000 nucléotides par seconde ce qui provoquait des problèmes d’acquisitions des signaux et donc des erreurs, sachant que l’objectif étant de ne pas dépasser les 400 bases / seconde, seuil au-delà duquel le capture devient fou…
Le 3 mai 2012, Oxford Nanopore annonce une collecte de fonds de 31,4 millions de livres (environ 50,8 millions de dollars). Encore plus de fond pour un séquenceur qui deviendrait pour un peu, un gouffre financier… « Ce tour de table a permis une levée de fonds dont la quasi-totalité provient d’investisseurs existants, ces fonds permettront un développement de l’entreprise, comprenant le développement de notre infrastructure, un renforcement de nos forces de vente, une optimisation de la fabrication et la poursuite de la R & D » a déclaré le Dr Gordon Sanghera, chef de la direction d’Oxford Nanopore. Oxford Nanopore se préparerait donc (enfin) à vendre ses produits qui sont attendus pour la fin d’année 2012. Phénomène plutôt rassurant pour la société anglaise, elle bénéficie de la confiance renouvelée de ces investisseurs, plus informés que nous sur ce que renferment (vraiment) ses tiroirs.
Eviter l’écueil d’un PacBio, trop cher, commettant trop d’erreurs, arrivé pour occuper le marché balbutiant du séquençage troisième génération, semble être la marque d’Oxford Nanopore -une société qui prend son temps. Après la possibilité de séquencer des molécules d’ADN à l’état natif, de taille très longue, en un temps record, il semble qu’Oxford Nanopore, avec ce nouvel appel de fonds, ficelle sa stratégie commerciale pour un lancement en grande pompe de leurs 2 références : le GridION & le MinION, la clé USB qui séquence dont vous pouvez voir la photographie ci-contre
Voici un documentaire diffusé sur Arte qui aborde en un peu plus de 50 minutes la biologie synthétique. Laetita Ohnona, la réalisatrice du film, pondère les interventions des Craig Venter et autres ingénieurs du MIT, technoscientistes par plusieurs interventions d’un lanceur d’alerte, Jim Thomas, filmé devant une campagne rassurante qui contraste avec l’univers d’un laboratoire. Ce documentaire très pédagogique (à mes yeux, il s’agit de sa principale qualité), consacre les ingénieurs face aux chercheurs -de la recherche appliquée vers la recherche fondamentale, en quelque sorte. Ainsi des parallèles sont réalisés entre des Steve Jobs & Bill Gates, deux personnages ayant révolutionné les applications liées à l’informatique et des Randy Rettberg & Tom Knight (co-fondateurs du prix Igem), des ingénieurs-chercheurs ayant œuvré en informatique pour terminer leur carrière dans les biotechnologies.
L’expérience de Philippe Marlière est développée en fin de documentaire pour apporter un début de solution au contrôle des organismes synthétiques comme outils de production.
Ce documentaire avivera la curiosité des scientifiques en herbe attiré par l’image d’Épinal de biogeek construisant un biofermenteur dans le garage de papa, effraiera les sceptiques, et très certainement produira un peu ces deux effets sur les initiés. On pourra simplement regretter l’absence d’un regard bioéthique dans ce documentaire qui permettrait de prendre un certain recul, évitant les allers-retours entre fascination technologique et peur de fin du monde, un monde ravagé par des bactéries tueuses luminescentes…
Ci-dessous : le synopsis d’Arte concernant ce documentaire
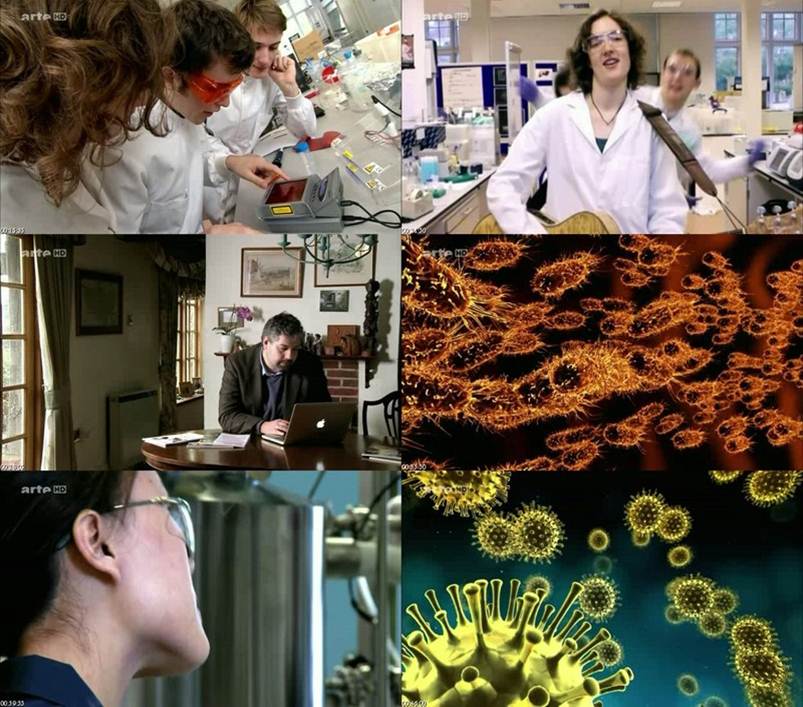
Les spécialistes sont unanimes : la biologie connaît une révolution aussi décisive que la découverte de l’ADN ou le séquençage complet du génome humain. La biologie de synthèse doit permettre à moyen terme à l’homme de se faire démiurge, pour écrire des séquences partielles ou entières d’ADN – et donc créer ainsi artificiellement la vie. Une perspective tellement nouvelle qu’elle suscite des vocations en dehors des laboratoires eux-mêmes. Dans de simples garages ou des hangars, les « biohackers » sont aujourd’hui capables d’assembler des séquences d’ADN synthétiques (via des DNA cassettes ou biobricks disponibles sur Internet). Peut-être donneront-ils vie à de nouvelles cellules, voire à des organismes entiers. Certains experts posent la question sans détour : l’homme va-t-il, pour la première fois, prendre la main sur l’évolution naturelle des espèces ? Et si oui, quelles seront les conséquences pour les écosystèmes les plus fragiles, et l’équilibre des espèces vivantes ? De nombreux acteurs, dont les plus gros laboratoires, investissent en tout cas dans la biologie de synthèse, jusqu’à Bill Gates, qui finance un programme colossal contre la malaria reposant sur elle. C’est cette révolution en marche que ce film souhaite montrer pour la première fois, en partant à la rencontre de ceux qui la portent.
(France, 2012, 52mn)
ARTE
Date de première diffusion : Jeudi 26 avr. 2012, 22h25
Date(s) de rediffusion : Samedi 5 mai 2012, 10h45
Vidéo disponible sur : http://videos.arte.tv/fr/videos/fabriquer_le_vivant-6609804.html
Vous aurez noté que le tour de France de Galaxy ne visite qu’un axe Perpignan-Lyon-Paris -loin de faire le tour de notre hexagone- on peut se réjouir de ce type d’initiatives. Galaxy en tournée un évènement dont vous trouverez quelques détails dans la suite de ce petit article…
 Lors de la visite de trois villes françaises des ateliers seront tenus à Perpignan, Lyon et Paris. L’inscription est gratuite, mais l’espace est limité et l’inscription pour chaque atelier sera arrêtée dès que les salles accueillant la tournée de Galaxy seront bondées.
Lors de la visite de trois villes françaises des ateliers seront tenus à Perpignan, Lyon et Paris. L’inscription est gratuite, mais l’espace est limité et l’inscription pour chaque atelier sera arrêtée dès que les salles accueillant la tournée de Galaxy seront bondées.
Le programme est disponible en suivant le lien ci-dessous :
http://wiki.g2.bx.psu.edu/Events/GalaxyTourDeFrance2012
28 mai: Perpignan
30 Mai: Lyon
1 juin: Institut Curie Amphithéatre Constant Burg, 12 rue Lhomond, 75005 Paris, France
Galaxy pour les biologistes :
9:00-12:00
Concepts de base: interface, historique, workflow
L’analyse des données NGS : découverte de polymorphismes, ChIP-seq. ARN-seq
En utilisant votre propre instance sur Cloud
Publication de « résultats supplémentaires » à l’aide des pages de Galaxy
Galaxy pour les développeurs :
14:00-17:00
Galaxy l’architecture
Outils pour le système Galaxy, Galaxy « entrepôt d’outils »
API
Exécution des sites de production Galaxy: infrastructure, planification de « jobs », de données et de gestion des utilisateurs
Cette tournée est à l’image de Galaxy : satisfaisante pour l’utilisateur biologiste qui se sert de cette « plateforme multimodale » comme outil d’analyse au bio-informaticien et informaticien qui intègre ses propres outils à Galaxy, cet outil chéri de Gaël tient, par la communauté des personnes qui l’anime toutes ses promesses.
Voici l’arrivée et la mise en exploitation du premier Ion Proton (Life Technologie) au Baylor College of Medicine à Houston.
36 heures entre la réception et la génération des premières données (avec des préparations de librairies réalisées en amont de la réception de la machine…).
Une présentation assez sympathique et ludique de la machine de Jonathan Rothberg… en avant première.
 A quelques jours du premier tour, cet article vous propose d’aborder les propositions d’orientations de la recherche scientifique des 5 courants majeurs participant aux présidentielles de 2012.
A quelques jours du premier tour, cet article vous propose d’aborder les propositions d’orientations de la recherche scientifique des 5 courants majeurs participant aux présidentielles de 2012.
Nous allons procéder en partant de la gauche à la droite frontistes en passant par des nuances de rose, orange et bleue : du « pour en finir avec les Bidulex » de J.L.Mélenchon, à la préférence de la langue française dans les communications scientifiques prônée par M. Le Pen.
– Front de Gauche – le candidat J.L. Mélenchon par l’intermédiaire du site Enseignement Supérieur & Recherche – appels Front de Gauche, remet la notion de service public au centre de la politique de la recherche française. Le Front de Gauche dresse un triste bilan de la politique gouvernementale en mettant à mal la notion d’excellence : « Jamais le potentiel universitaire n’a été ainsi saccagé sous le prétexte mystificateur d’une “excellence” qui n’avoue pas ses véritables critères. » La multiplication des sources de financements et la structuration des organismes en poupées gigognes sont dénoncées : « Les Idex, Labex et autres « Bidulex » visent aujourd’hui à créer des territoires d’exception au sein de la République pour mieux conforter la concurrence libre et non faussée internationale. » L’ex-ministre de l’Enseignement professionnel taille un costard à l’ANR qu’il souhaite « dissoudre » (pour le remplacer par quoi ?). J.L. Mélenchon propose de transformer les IDEX qui lui paraissent participer d’une concurrence entre les intervenants de la recherche scientifique, en pôles de coopération scientifique. Le projet inclus le recrutement de 5000 emplois statutaires par an sur la durée du quinquennat.
– Parti Socialiste – Le programme du PS concernant la recherche scientifique reste quelque peu flou. Peu de mots dans les 60 engagements de François Hollande sont associés à la recherche scientifique (le programme du PS est délibérément tourné vers l’enseignement supérieur plus que vers l’aspect recherche de ce portefeuille ministériel). Malgré tout, quelques propositions peuvent être associées à la recherche scientifique : vers un plus d’autonomie et vers une recherche compétitive au niveau international- très proche sur ce sujet de la vision d’un UMP de début de mandat présidentiel de 2007 : « nous donnerons les moyens pérennes nécessaires à l’autonomie et au rayonnement des équipes, des laboratoires et des Universités ». Contrairement au parti du tribun du front de gauche, F. Hollande n’oublie pas de satisfaire les velléités scientifiques des industriels, ainsi, le projet du P.S. prévoit la création d’une Banque publique d’investissement, qui investira dans la recherche et l’innovation, soutiendra les PME-PMI, prendra des participations dans les activités stratégiques et les filières industrielles d’avenir (quelles sont elles précisément ?), et dont les moyens seront mobilisés sous la forme de fonds régionaux en co-pilotage avec les Régions. Les modalités d’obtention du crédit impôt recherche seront rendus plus simples (comment ?). Par l’intermédiaire de Vincent Peillon, le PS propose des solutions pour les étudiants et la modification de la loi LRU. Un programme du PS centré sur le financement de la recherche privée et de l’amélioration des conditions pour dispenser un enseignement supérieur de qualité, ouvert au plus grand nombre.
– MoDem- Nous arrivons ici au point de symétrie de notre tour d’horizon avec les (la?) propositions du Modem, le parti de F. Bayrou pour ce qui concerne la recherche scientifique dont voici la mesure phare : la création d’un crédit d’impôt innovation, parallèle au crédit impôt recherche… des fonds destinés à la recherche privée. Le programme de l’hyper-centre s’attarde (ceci n’est pas une critique) sur la problématique de l’enseignement mais oublie de parler de politique de la recherche scientifique… Mais en cherchant, on trouve quelques éléments : « veillons à ne pas axer nos politiques de recherche sur la base d’indicateurs d’origine asiatique qui certes favorise la diffusion des nouveaux savoirs par la publication scientifique, mais qui en pratique sont utilisés localement pour exacerber les rivalités entre équipes de recherche« … tiré du programme officiel du Modem pour l’enseignement et la recherche scientifique dont le chantre est Denis Badré, personnalité qui semble être l’interlocuteur des sujets « enseignement supérieur et recherche » du parti centriste.
– UMP – Au tour du programme du parti au pouvoir actuellement. Là aussi l’accent est mis sur l’innovation, aux talents et aux marchés, partant du principe qu’une recherche forte, dans une France forte vient surtout en aide aux PME et grandes industries pour améliorer leur compétitivité internationale, exemple :
– Le premier dépôt de brevet doit être gratuit pour les PME. Une partie des financements européens pour la recherche (Programme-cadre de recherche et de développement) seraient conditionnés à la participation de PME aux projets de recherche.
– Le parti présidentiel souhaite donc maintenir le crédit impôt-recherche. Par ailleurs, une meilleure valorisation de la recherche publique est invoquée, en favorisant les liens entre les universités et les entreprises et en intéressant les chercheurs publics aux retombées financières de leurs découvertes.
Enfin, la volonté de soutenir l’ambition (comment ?) de notre recherche et de notre industrie pour proposer de nouvelles thérapies, générer de la croissance économique au service d’une médecine humaine et contribuer au rayonnement de la médecine française…
Note : l’article que vous êtes en train de lire a été réalisé avant la parution officielle du programme de N. Sarkozy (programme qui paraitra jeudi prochain – 15 jours avant le premier tour). Vous pouvez avoir une vision du bilan du quinquennat de N. Sarkozy par le biais de la plume de Bruno Chaudret (chimiste et membre de l’Académie des sciences, élu par ses pairs, est Président du Conseil scientifique du CNRS).
– Front National – Le FN envisage de consacrer 3% du PIB d’ici 2017 à la recherche (pour information actuellement la France consacre 2,15 % de son PIB à la recherche -46% à la charge de l’Etat et 54% à la charge du secteur privé). Marine Le Pen propose de provoquer des états-généraux (un grenelle de plus?) de la recherche « pour fixer les priorités, pour définir les grands axes stratégiques, pour déterminer et mettre en œuvre les réformes structurelles permettant un rapprochement entre grandes écoles, universités et organismes de recherche. Cette réflexion de fond réunira tous les acteurs de la recherche, sachant que la situation économique de la France est telle que l’augmentation souhaitable des crédits ne pourra intervenir que très progressivement. En attendant, des choix devront être faits et des priorités fixées. » Une proposition encore un peu plus floue invoque l’augmentation du budget alloué à la recherche fondamentale dès lors que « la situation des finances publiques se rétablira ». Marine Le Pen conforte les organismes d’évaluation et d’attribution de finances de la recherche scientifique : « Les agences de financement, à l’instar de l’ANR (Agence Nationale de Recherche), verront leurs conseils scientifiques élargis et seront appelées à plus de transparence sur les conditions d’attribution des aides qui devront respecter des critères strictement scientifiques et s’inscrire en conformité avec les priorités fixées par la Nation. » Enfin, on ne peut passer à côté de l’humour sous-jacent dans la proposition suivante : « Les meilleurs chercheurs étrangers seront attirés dans le cadre d’une politique d’immigration ultra-sélective exclusivement centrée sur les talents (l’objectif global est de ramener l’immigration légale de 200 000 titres de séjour par an à 10 000 en fin de mandat)« . Pour conclure, M Le Pen souhaite favoriser l’usage de la langue française dans les colloques et publications scientifiques.
La recherche est une thématique mineure de la campagne des présidentielles de 2012. Malgré tout, ce thème fait l’objet de clivages partisans très archétypaux : la vision d’une coopération entre groupes de recherche d’un Mélenchon s’oppose à une compétition inter-groupes d’un Sarkozy. Il est étonnant d’observer que les partis les plus éloignés du centre développent largement plus ce thème. Thème de la recherche française que les PS, MoDem et UMP laissent de côté au profit de sujets plus « économiques »… pour les partis souhaitant gouverner il est certainement assez peu « rentable » en temps d’élection et de crise d’aborder un sujet aussi technique et glouton en dépenses publiques.
En pleine guerre froide des compagnies de biotechnologies, développeuses et vendeuses de matériel de séquençage… une fuite de documents est organisée. Le tout pour fournir aux personnes prescriptrices ou décideuses d’un futur achat de séquenceur, les arguments pour orienter ou justifier leur choix… parfois même leur mauvaise foi.

En cliquant sur la volute nucléique (depuis le 30/08/2012 – ce lien est censuré par Illumina- cf. commentaires de ce même article) ci-dessus vous aurez accès à un vrai-faux document confidentiel fourni par Illumina. Ce document assez bien réalisé a devancé celui de Life Technologies présenté dans notre article précédent. Il met l’accent sur le bénéfice, au niveau de la qualité des données générées, que procure un MiSeq (Illumina) par rapport à un PGM (Ion Torrent, Life Technologies)
Un document paru dans la Ion Community (site de partage autour de la technologie Ion Torrent et Ion Proton de Life Technologies) commence à faire parler de lui. En effet, des scientifiques de Life Technologies montrent et démontrent que le MiSeq d’Illumina produit (aussi) des erreurs au niveau des homopolymères.
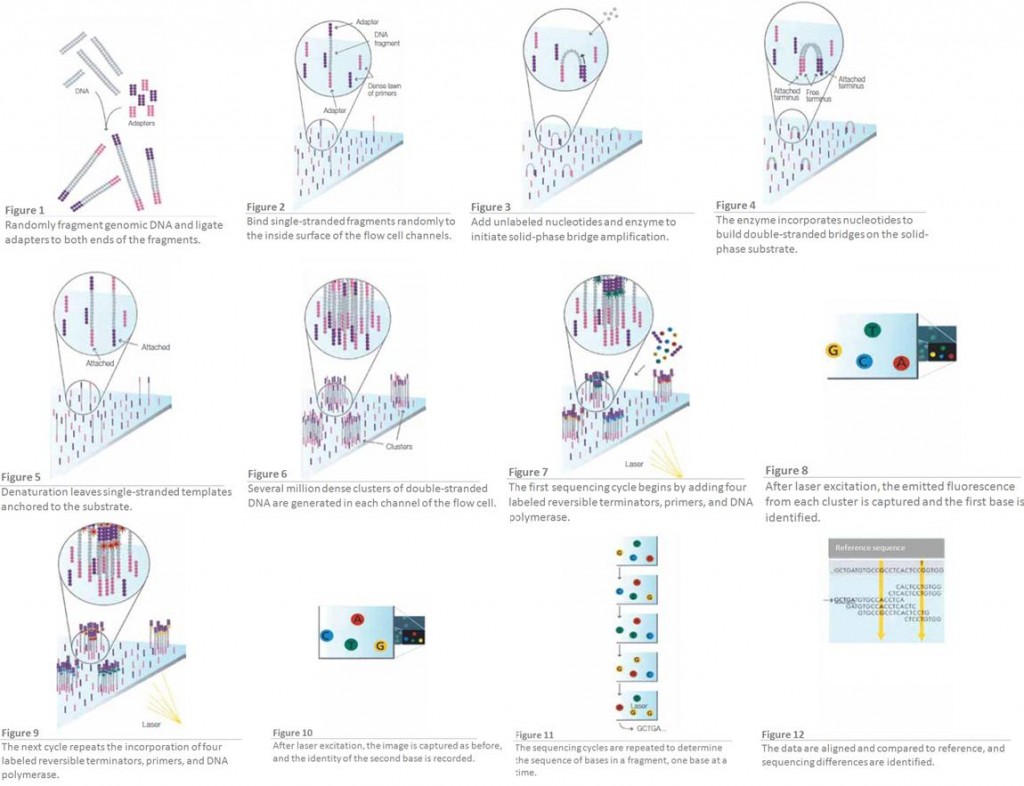
Nous savions depuis longtemps que les séquenceurs de type 454 ou Ion Torrent montraient des biais quant à détermination correcte de ce type de séquences… Ici, pour la première fois les méthodes de SBS (Sequencing By Syntesis) dont le principe pour la technologie Illumina est rappelée par le schéma disponible ci-dessous, montrent des biais étonnement importants pour la juste détermination de séquences adjacentes d’homopolymères (particulièrement concernant les régions GC % riches). La note qui met le feu dans l’argumentaire commercial d’Illumina est disponible ici-même. Une hypothèse quant à la génération de ce type d’erreurs est formulée.
Nous vous laissons le soin de lire la note, intéressante malgré la partialité de la source. La démonstration quoique scientifique, montre l’âpreté de la bataille qui se joue entre les acteurs majeurs du séquençage de paillasse de deuxième génération.
 Cet article est l’occasion de mettre en avant un site plutôt fourni, SEQanswers… un jeu de mots pour une communauté d’utilisateurs de technologie de séquençage haut-débit. Ce site, un peu bouillon, fondé en 2007 par Eric Olivares (qui a travaillé pour Pacific Biosciences) s’adresse aux biologistes moléculaires plus qu’aux bio-informaticiens. Malgré tout, le lien que nous vous présentons ici, renvoie sur la partie Wiki du site SEQanswers. Cette page liste et ordonne en fonction de leurs domaines d’applications les logiciels (gratuits et commerciaux) utiles pour le devenir de vos reads produits par séquençage haut-débit : http://seqanswers.com/wiki/Software/
Cet article est l’occasion de mettre en avant un site plutôt fourni, SEQanswers… un jeu de mots pour une communauté d’utilisateurs de technologie de séquençage haut-débit. Ce site, un peu bouillon, fondé en 2007 par Eric Olivares (qui a travaillé pour Pacific Biosciences) s’adresse aux biologistes moléculaires plus qu’aux bio-informaticiens. Malgré tout, le lien que nous vous présentons ici, renvoie sur la partie Wiki du site SEQanswers. Cette page liste et ordonne en fonction de leurs domaines d’applications les logiciels (gratuits et commerciaux) utiles pour le devenir de vos reads produits par séquençage haut-débit : http://seqanswers.com/wiki/Software/
Cette page est plutôt bien renseignée et vous donnera un large choix de logiciels : vous y trouverez des assemblers de novo, des logiciels pour réaliser du RNAseq (quantification), des logiciels permettant de trouver des pics après ChipSeq… peu de logiciels indispensables sont absents de cette liste qui comporte un peu moins de 500 logiciels…
La paléontologie, la science des fossiles et des traces de vie du passé, use de méthodes de biologie moléculaire de pointe qui pallient les effets du temps qui passe…
Afin d’introduire ce premier article traitant de paléogénomique, les moyens de la biologie moléculaire au service de la paléontologie, une vidéo amuse-bouche (Auteur(s) : Eva-Maria Geigl, Réalisation : Samia Serri, Production : Université Paris Diderot, Durée : 17 minutes 40 secondes) est disponible en usant du fameux clic gauche sur la capture d’image ci-dessous. Cette vidéo vaut surtout pour l’accent mis sur les précautions indispensables pour l’étude d’un échantillon précieux fossilisé… et dont l’ADN, peu abondant, peut être fragmenté. En outre, des mesures simples mais draconiennes permettent de limiter les sources de contaminations, quand l’ADN moderne peut polluer l’ADN fossile. Le port de sur-chausses, de masque et les changements de blouses, le non croisement des échantillons avant et après amplification sont autant de précautions mises en avant dans cette vidéo… une occasion de visiter virtuellement les laboratoire de l’Institut Jacques Monod.
L’une des problématiques liées à l’étude de l’ADN « fossile » réside dans sa faible quantité disponible. Plusieurs méthodes de biologie moléculaire ont été envisagées pour amplifier ce matériel génétique afin d’en permettre l’expertise. Une publication dans BMC Genomics de 2006, Assessment of whole genome amplification-induced bias throughhigh-throughput, massively parallel whole genome sequencing, relate la comparaison de 3 méthodes d’amplifications pan-génomiques (méthodes WGA pour Wide Genome Amplification) d’ADN qui pourra devenir ensuite la matrice suffisante d’un séquençage haut-débit.
– la PEP-PCR (Primer Extension Preamplification-PCR) : cette technique fait intervenir des amorces aléatoires aux conditions d’appariement à basse température (low melting temperature) qui initieront la PCR
référence : Zhang, L. et al. (1992) Whole genome amplification from a single cell: Implications for genetic analysis. Proc. Natl. Acad. Sci. USA 89, 5847
– la DOP-PCR (Degenerate Oligonucleotide Primed-PCR) : cette technique, quant à elle, fait intervenir des amorces semi-dégénérées (de type : CGACTCGAGNNNNNNATGTGG) qui ont une température d’hybridation supérieure à celles utilisées dans la PEP-PCR
référence : Telenius, H. et al. (1992) Degenerate oligonucleotide-primed PCR: general amplification of target DNA by a single degenerate primer. Genomics 13, 718.
L’utilisation d’une Taq PCR limite la taille des fragments néo-synthétisés qui ne dépassent guère 3 kb. En outre, ces deux techniques, à l’instar de ce qui peut être démontré dans la publication de BMC Genomics 2006 (mentionnée ci-dessus), induisent des erreurs de séquences accompagnées de nombreux biais d’amplification (certaines régions ne sont pas amplifiées au profit de régions qui deviennent, de fait, sur-représentées).
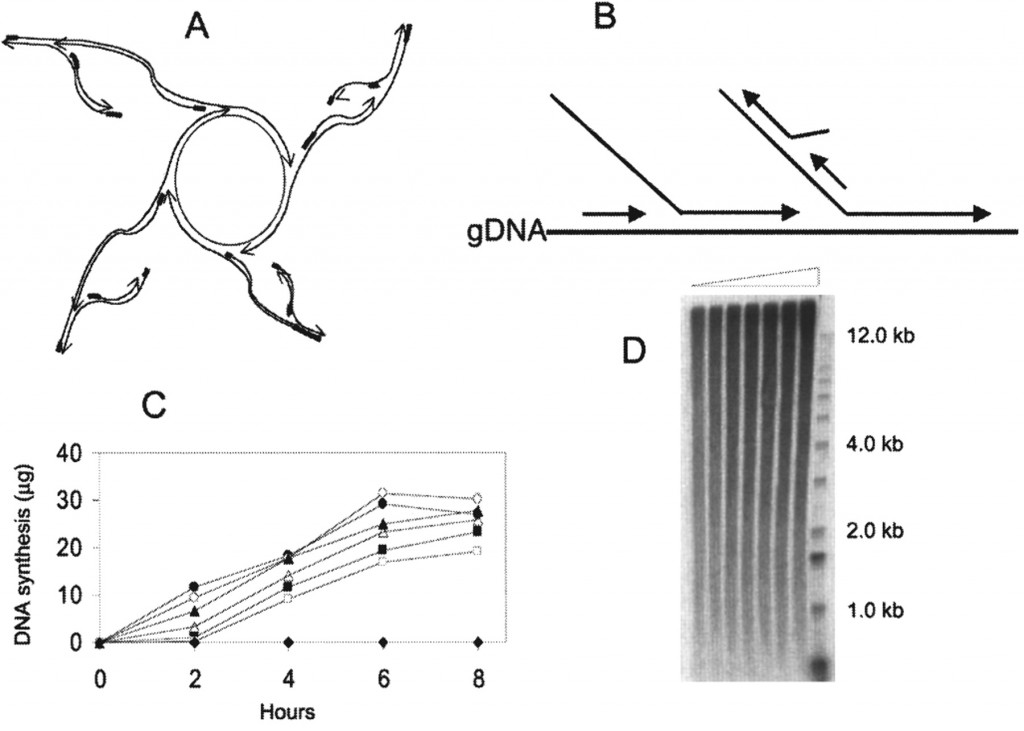
– la MDA (Multiple Displacement Amplification) : cette amplification iso-thermique fait intervenir des amorces aléatoires de type hexamères et une enzyme, la phi29. Le type d’amplification générée est schématisées sur la figure ci-dessous. L’enzyme surfe à partir du brin néo-synthétisé, déplace un brin complémentaire pour continuer sa synthèse. Ainsi, les brins générés par cette technique peuvent atteindre 100 kb. En outre, la phi29 possède une activité 3′ -> 5′ de relecture (proofreading) lui conférant un taux d’erreur 100 fois moindre que ceux constatés pour des Taq polymérases classiquement utilisées dans les techniques de PEP- ou DOP-PCR
source : Cold Spring Harb Protoc 2011.2011: pdb.prot5552 (la légende originale de la figure est disponible en cliquant sur celle-ci)
Ces techniques d’amplification pangénomique ont rendu possible l’étude d’ADN anciens et peu abondants et tout naturellement elles ont trouvé leur place dans la boîte à outils moléculaires des paléogénéticiens. Cependant, la révolution des séquençages haut-débit (dont nous avons abordé le sujet à plusieurs reprises) laisse entrevoir un nouveau champ des possibles pour l’étude des ADN fossiles. Au fond, des technologies telles que celle développée par Helicos Biosciences, trouvent ici un réel champ d’application à l’instar de ce que développe la publication True single-molecule DNA sequencing of a pleistocene horse bone de Genome Research, 2011- nulle nécessité d’amplifier la matrice de départ. Cette publication compare des technologies de séquençage de 2ème et 3ème générations (GaIIx et Helicos) appliquées au séquençage de l’ADN isolé à partir d’un os de cheval pleistocène conservé dans permafrost. Le séquençage « single molecule« , une chance pour la paléogénomique !
- des fiches logiciels (classement, descriptions et lien pointant vers l’hébergeur de ceux-ci)
- des fiches ressources (site internet, évènements, documents utiles…)
- mutualiser les compétences sur les logiciels
- promouvoir les développements internes
- animer une communauté autour du logiciel
- promouvoir l’usage des logiciels libres et la contribution à leur élaboration
Qui sommes nous?
Christophe Audebert [@]
 En charge de la plateforme génomique
du département recherche et développement
de la société Gènes Diffusion .
En charge de la plateforme génomique
du département recherche et développement
de la société Gènes Diffusion .
Renaud Blervaque [@]
 Biologiste moléculaire, chargé d'études génomiques.
Biologiste moléculaire, chargé d'études génomiques.
Gaël Even [@]
 Responsable bioinformatique au sein
du département recherche et développement de la société Gènes Diffusion.
Responsable bioinformatique au sein
du département recherche et développement de la société Gènes Diffusion.
Catégories
- Analyse de données (14)
- Automatisation (5)
- Bioinformatique (27)
- Biologie (56)
- biologie transverse (35)
- Biotechnologie (30)
- Chronique littéraire (8)
- Comparatif (6)
- Diagnostic (8)
- Economie (17)
- Epidemiologie (2)
- Evénement (17)
- Formation (3)
- Gestion de projet (5)
- Grille de calcul (1)
- Intégration (5)
- Logiciels (8)
- Médecine (14)
- politique de la recherche (17)
- Recherche (21)
- Séquençage (70)
- Séquenceur (39)
- Uncategorized (25)
- Workflow (4)
Accès rapide aux articles
- Covid-19 : zoom sur les vaccins
- Comment l’ADN pourrait être le stockage de données du futur
- COVID-19 : la data visualisation au service de la science
- COVID-19 : des explications et un point d’étape au 20 février 2020
- Pour mettre du vin dans son eau
- Des petits trous, toujours des petits trous…
- Qui serait candidat ?
- Un robot pour analyser vos données…
- Monde de dingue(s)
- L’art et la manière de développer une qPCR
- Un MOOC Coursera sur le WGS bactérien
- Chercheurs & enseignants-chercheurs, l’art du multitâche.
- Un jeu de données métagénomiques
- Facteur d’impact
- Microbiote & smart city : juxtaposition de tendances
Accès mensuels
- février 2021 (1)
- décembre 2020 (1)
- février 2020 (2)
- septembre 2019 (1)
- avril 2018 (2)
- décembre 2017 (1)
- novembre 2017 (2)
- juillet 2017 (2)
- juin 2017 (5)
- mai 2017 (4)
- avril 2017 (3)
- mars 2017 (1)
- janvier 2017 (2)
- décembre 2016 (3)
- novembre 2016 (4)
- octobre 2016 (2)
- septembre 2016 (2)
- août 2016 (3)
- juillet 2016 (2)
- juin 2016 (4)
- mai 2016 (3)
- mars 2016 (1)
- novembre 2015 (2)
- avril 2015 (1)
- novembre 2014 (1)
- septembre 2014 (1)
- juillet 2014 (1)
- juin 2014 (1)
- mai 2014 (1)
- avril 2014 (1)
- mars 2014 (1)
- février 2014 (3)
- janvier 2014 (1)
- décembre 2013 (5)
- novembre 2013 (2)
- octobre 2013 (2)
- septembre 2013 (1)
- juillet 2013 (2)
- juin 2013 (2)
- mai 2013 (4)
- avril 2013 (2)
- mars 2013 (1)
- février 2013 (3)
- janvier 2013 (2)
- décembre 2012 (2)
- novembre 2012 (2)
- octobre 2012 (2)
- septembre 2012 (2)
- août 2012 (1)
- juillet 2012 (3)
- juin 2012 (5)
- mai 2012 (5)
- avril 2012 (6)
- mars 2012 (6)
- février 2012 (8)
- janvier 2012 (6)
- décembre 2011 (5)
- novembre 2011 (6)
- octobre 2011 (6)
- septembre 2011 (7)
- août 2011 (5)
- juillet 2011 (8)
Pages